Hoy a habido cierta difusión en los medios sobre un estudio publicado hoy jueves en Nature, indicando que se había descubierto los determinantes genéticos que influyen en que una persona pueda sufrir un COVID severo. El enlace al artículo lo encontráis al final.
Voy a intentar explicar lo que él artículo a encontrado que es unos grados menos de lo que se ha publicitado en los medios.
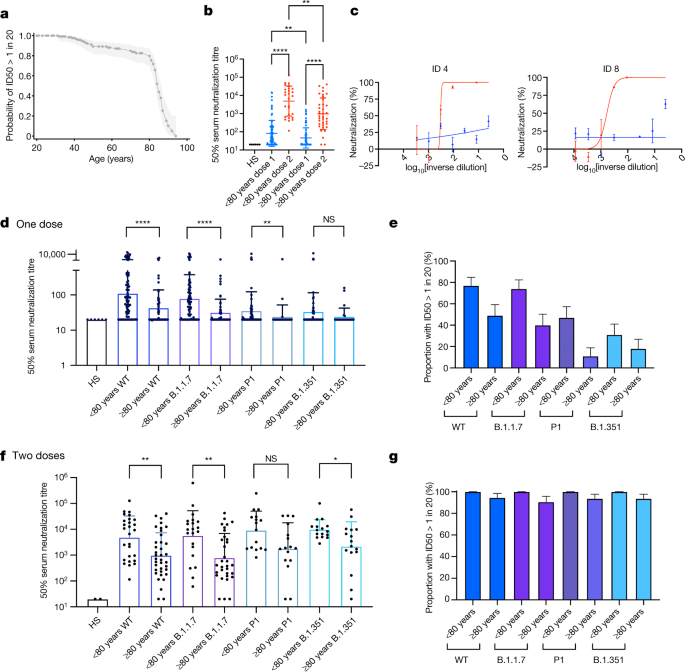
Básicamente los autores han estudiado que variaciones en regiones de los cromosomas estarían asociados a una mayor probabilidad de contraer la COVID o de que esta sea más severa. Este aumento en las probabilidades suelen ser modestas, aunque en algunos casos pueden llegar a un 50% (lo que ya no parece tan modesto). Algunas de estas regiones cromosómicas no tienen un gen que se haya identificado como el responsable de esta aumento en el riesgo. Pero en otros casos si que se han identificado potenciales genes. La identificación de estos genes no solamente puede permitir en el futuro determinar mediante análisis genético si una persona es más vulnerable a la COVID-19 sino que también permiten conocer mejor el alcance de la enfermedad e identificar potenciales dianas que puedan ser "atacadas" terapéuticamente.
| Susceptibility | 9–12 | ABO (determines blood group) | 9 |
| Susceptibility | 13–18 | SLC6A20 (interacts with ACE2 receptor, which mediates SARS-CoV-2 entry) | 3 |
| Severity. | 13–20 | IFNAR1/2 (part of cell receptor for interferon, proteins that bolster immune response) | 21 |
| Severity | 14–26 | OAS family (enzymes that digest viral RNA) | 12 |
| Severity | 17–36 | FOXP4 (involved in lung diseases) | 6 |
| Severity | 20–32 | DPP9 (enzyme involved in lung disease) | 19 |
| Severity | 29–59 | TYK2 (enzyme involved in interferon signalling) | 19 |
La segunda columna indica el aumento en el riesgo (susceptibilidad o severidad). La última columna es el cromosoma donde se encuentra esa region/gen asociada con la COVID-19.
Entre los genes asociados a una mayor susceptibilidad están los que determinan el grupo sanguíneo (ABO) y el SLC6A20 (que es un transportador de moléculas pequeñas no identificadas todavía) y que parece interacciones con ACE2, la puerta de entrada del virus a la célula.
Otros genes, como IFNAR1/2 y TYK2 están relacionados con los interferones que son moléculas que generamos con actividad antiviral. Otros están relacionados con patología pulmonar (FOXP4 - asociado a tumores en laringe y DPP9 - asociado a fibrosis pulmonar). OAS forma parte de una familia de proteínas que "destruyen el RNA vírico por lo que descensos en los niveles de estas proteínas pueden favorecer la infección. finalmente hay otras zonas en el genoma que parecen también relacionadas (no están en la tabla que he puesto) pero de las que se desconocen que genes que están en ellas pueden ser los importantes en esta asociación con la COVID-19.
Como curiosidad decir que hay un fármaco que se utiliza contra la artritis reumatoide, el baricitinib, que inhíbe la proteína TYK2. Ya se esta probando en ensayos si puede ser de ayuda frente a la COVID-19.